circRNA
Detailed infomation of each circRNA
Detail information of Niben101Scf02497g05005_circ_ig.1
| General Information | |
|---|---|
| CircRNA Name | Niben101Scf02497g05005_circ_ig.1 |
| ID in PlantcircBase | nbe_circ_000973 |
| Alias | NA |
| Organism | Nicotiana benthamiana |
| Position | chrNiben101Scf02497: 253296-255977 JBrowse» |
| Reference genome | Niben.genome.v1.0.1 |
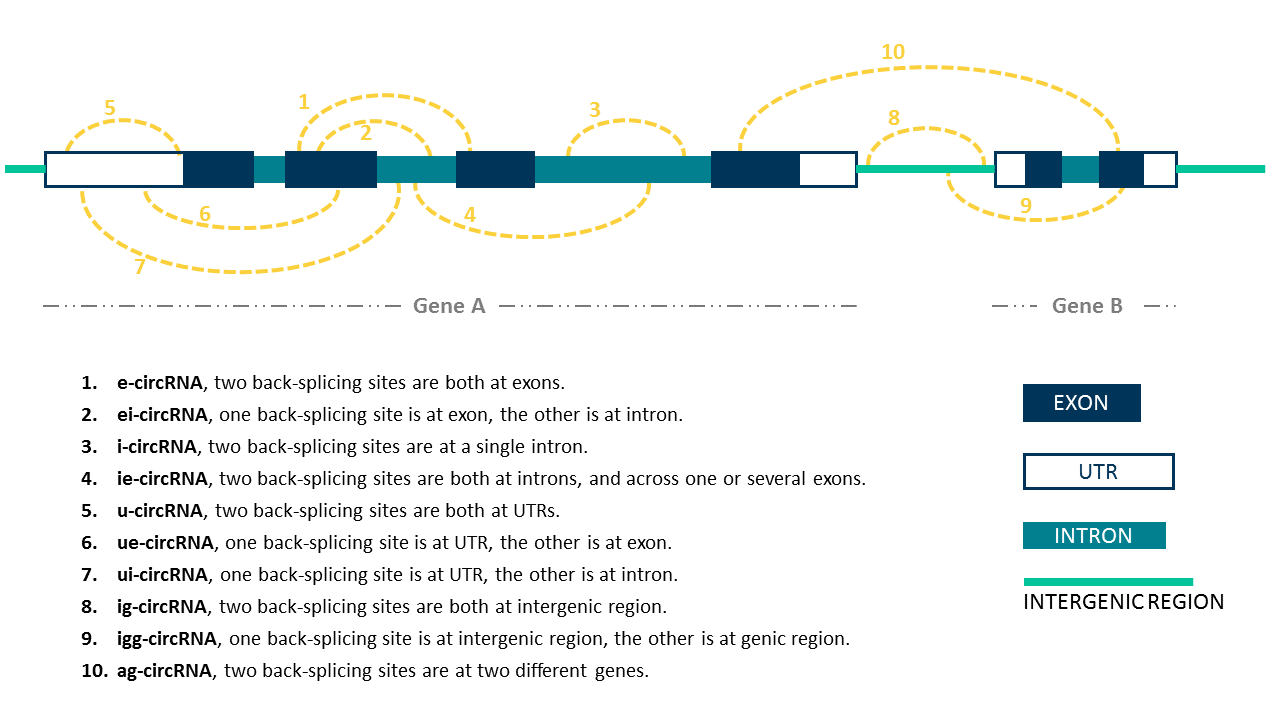
| Type | ig-circRNA |
| Identification method | DCC |
| Parent gene | NA |
| Parent gene annotation | NA |
| Parent gene strand | NA |
| Alternative splicing | NA |
| Support reads | NA |
| Tissues | leaf |
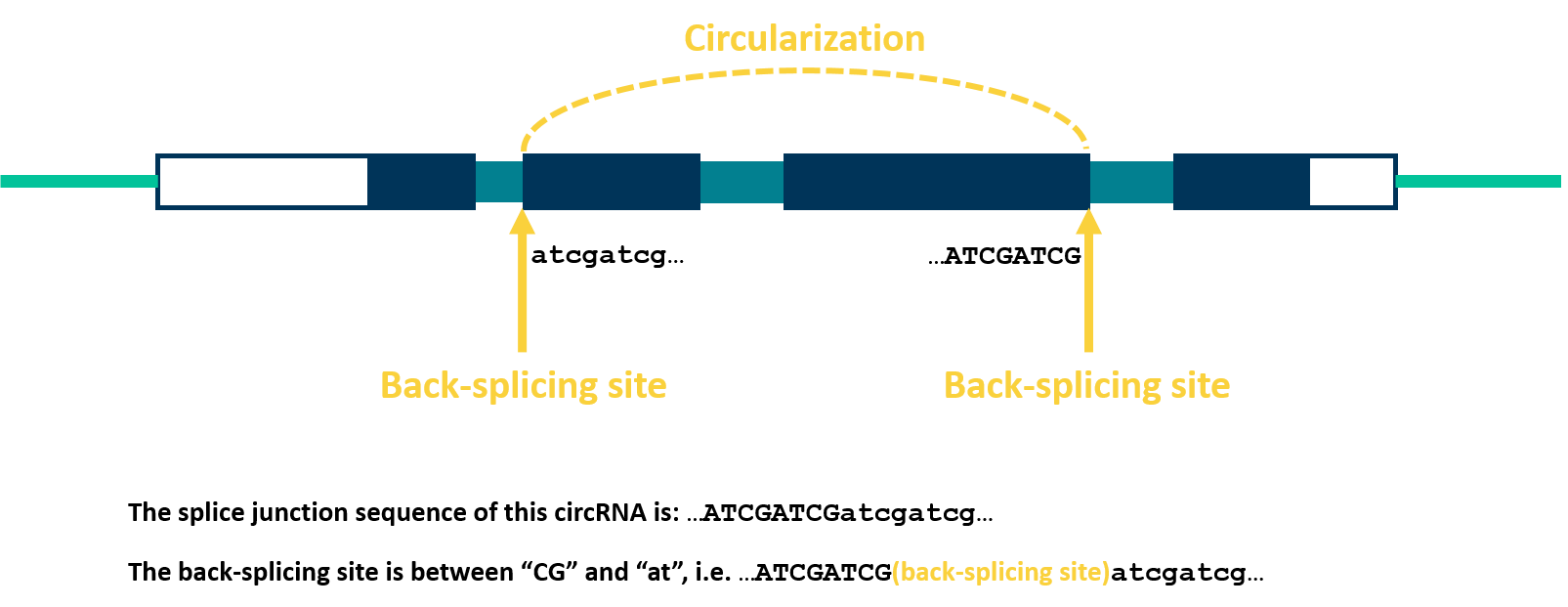
| Exon boundary | NA-NA |
| Splicing signals | GC-AA |
| Number of exons covered | NA |
| Conservation Information | |
|---|---|
| Conserved circRNAs | NA |
| PMCS |
| Functional Information | |
|---|---|
| Coding potential | NA |
| Potential coding position |
NA |
| Potential amino acid sequence |
NA |
| Sponge-miRNAs | NA |
| circRNA-miRNA-mRNA network | VISUALIZATION |
| Potential function description | NA |
| Other Information | |
|---|---|
| References | Guria et al., 2019 |